- 面议
起订量:
12204ES08 一步法DNA建库试剂盒
- 型号
- 12204ES08
该企业相似产品
企业简介
翌圣生物科技(上海)股份有限公司【Yeasen Biotechnology (Shanghai) Co., Ltd.】是一家以蛋白质改造和酶进化技术为驱动,聚焦生命科学产业链上游核心原料,从事分子、蛋白和细胞三大品类生物试剂的研发、生产与销售的高新技术企业,通过打通分子酶、蛋白、抗体、核酸、细胞的技术开发路径,成为国内少数同时覆盖三大品类生物试剂、兼备核心技术自主研发能力和规模化生产能力的高新技术企业,产品广泛应用于生命科学研究领域、诊断与检测领域和生物医药领域。
主营业务
公司凭借在蛋白质改造和酶进化领域的技术优势和深耕生物试剂行业多年积累的丰富经验,构建了品质优良、类型齐全、种类丰富的产品管线。自公司成立以来,公司研发、生产和销售的生物试剂超过3000种,涵盖分子、蛋白、细胞三大品类的生物试剂,能够满足客户多种类型生物试剂的一体化采购需求。公司核心产品覆盖qPCR系列、NGS系列、逆转录系列、核酸提取与纯化系列、PCR系列、分子克隆系列、体外转录系列、抗体、蛋白纯化系列、蛋白分析系列、重组蛋白、细胞分析系列、细胞培养系列、细胞转染系列、报告基因检测系列等多个品类的生物试剂,广泛应用于生命科学研究、诊断检测和生物医药等领域。
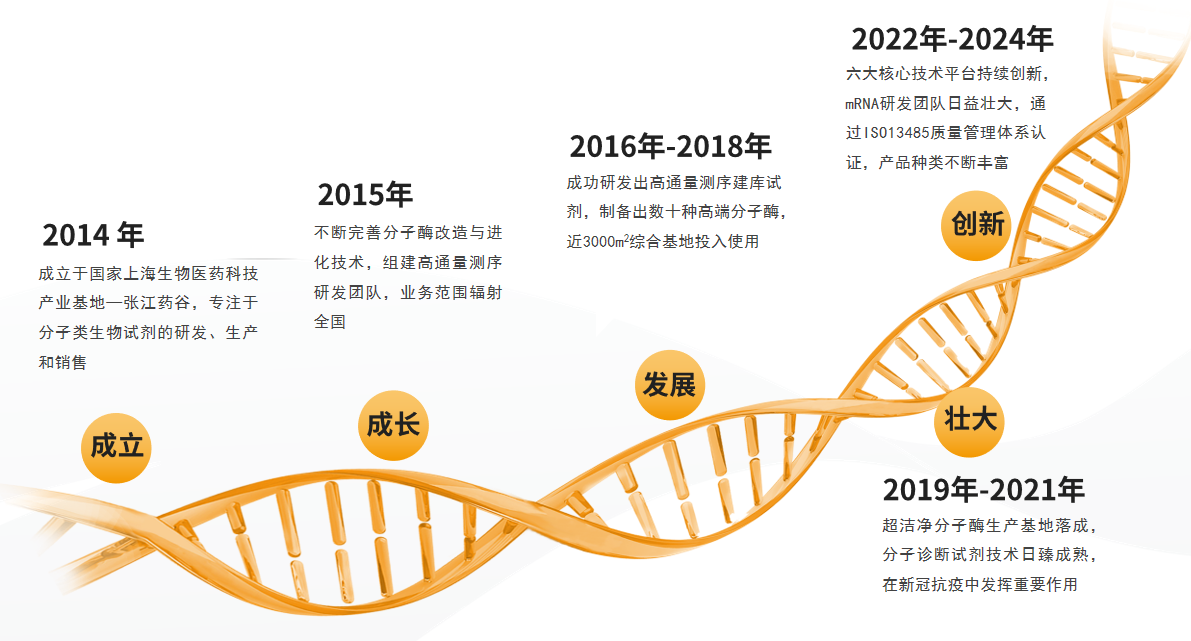
发展历程
荣誉资质
翌圣生物通过申请商标和软件著作权的方式保障核心技术和市场竞争力,不断加强公司品牌建设。截至2022年3月31日,公司已经获得授权18项(其中发明14项、实用新型1项、外观设计3项)和45项与生物试剂相关的软件著作权,拥有经国家知识产权局商标局核准的注册商标权37项以及4项境外注册商标,是国家高新技术企业和上海市专精特新企业。

创新平台
经过多年的产品研发技术经验的沉淀以及持续的研发创新,翌圣生物积极开展“产学研”合作,与拥有生物催化与酶领域国家重点实验室的湖北大学、拥有教育部工业生物领域重点研究基地的江南大学展开合作,优化生物试剂关键原料的生产和表达工艺。翌圣生物以基因工程技术、生物信息技术、细胞生物学技术、免疫学技术、生化分析技术等生命科学领域的共性生物技术为基础,建立了六大核心技术平台——双向分子酶理性设计与定向进化平台、密度发酵与超洁净纯化平台、分子诊断试剂关键原料研发平台、高通量测序建库试剂创新研发平台、高性能单克隆抗体研发平台和mRNA医药应用研发平台,目前已经自主研发出20项核心技术,打通分子酶、蛋白、抗体、核酸、细胞的技术开发路径,覆盖技术研发、产品升级、规模生产和质量控制等生物试剂研发和生产的各关键环节。




工业化生产
翌圣生物拥有按照准GMP 标准建设运营的工业化生产基地,配有吨级发酵线、工业级 AKTA 纯化线和全自动包装线。同时,公司通过了ISO 13485:2016质量管理体系认证,从原料控制、生产管理、质检管控、仓储运输等对生产线进行360度管理监督,保证产品过程的可控制性及可追溯性,竭尽全力为您提供可靠的产品。

客户服务
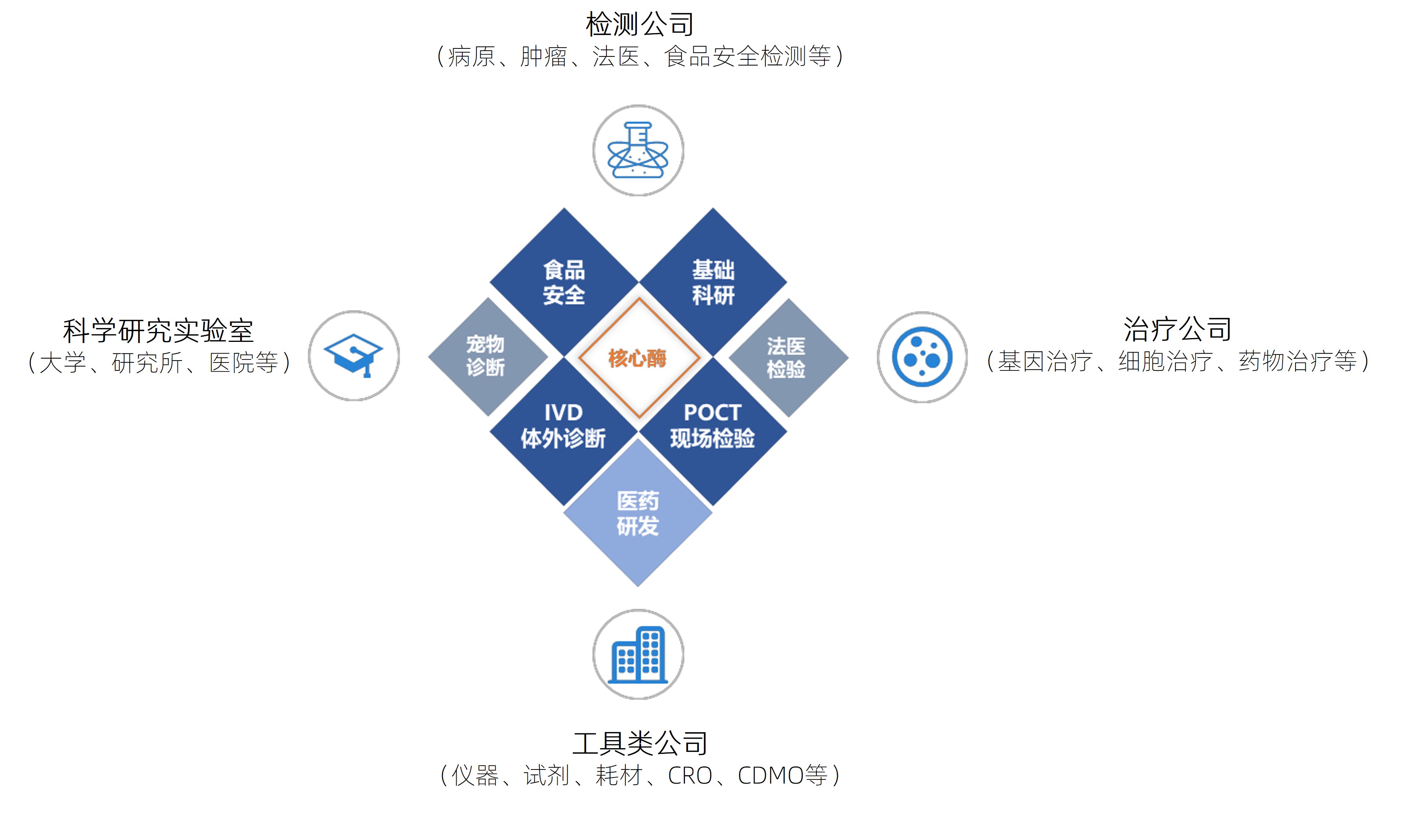
翌圣生物凭借优质稳定的产品质量、高效及时的响应能力、快速稳定的交付能力和周到完备的售后服务获得了众多科研用户和工业用户的认可,为检测公司、治疗公司、工具类公司和科学研究实验室提供应用于科学研究、体外诊断、基因测序、生物医药等的生物试剂。与中国科学院、清华大学、北京大学、复旦大学、上海交通大学、浙江大学等顶尖科研院所和华大基因、恒瑞医药、药明康德、之江生物、圣湘生物、斯微生物、金斯瑞、思路迪等工业客户建立了稳定、紧密的合作关系,公司产品被多次使用在Nature、Science、Cell等国际顶级期刊论文发表中。
公司企业文化
帮助客户创造价值,让世界更健康更快乐
◎ 成为生命科学工具领域全球Top⑩
◎ 具备驱动产业变革的技术创新能力
◎ 拥有一支持续学习型的翌圣铁军
翌圣生物始终秉承“帮助客户创造价值,让世界更健康更快乐”的使命,专注于技术创新和产品升级,不断拓展核心技术的应用领域,为客户提供更为的产品与服务,助力我国打造自主可控的生物试剂产业链。同时,翌圣生物将进一步推进国际化战略,继续布局和拓展海外市场,为全球生物试剂产业发展贡献力量。
详细信息
产品信息
产品名称 | 产品编号 | 规格 | 价格(元) |
Hieff NGS® OnePot II DNA Library Prep Kit for Illumina® | 12204ES08 | 8 T | 2578.10 |
12204ES24 | 24 T | 5308.10 | |
12204ES96 | 96 T | 20064.10 |
产品描述
Hieff NGS® OnePot II DNA Library Prep Kit for Illumina®是针对Illumina®高通量测序平台专业开发设计的新一代酶切法建库试剂盒。与传统的建库法比较,本品采用高质量的片段化酶,摆脱了繁琐的超声过程,同时简化了操作流程,将片段化模块与末端修复模块合二为一,极大的降低了建库的时间和成本。本试剂盒具有优秀的文库转化率,可应用于常规动植物基因组、微生物基因组等样本,同时能兼容FFPE DNA样本的建库。经测序验证,不同GC含量的样本,均可获得优异的测序结果,文库覆盖度高,均一性好,偏好性低,使建库变得更加简单高效。
适用500 pg-1 μg的基因组DNA、全长cDNA等样本
高质量片段化酶,可随机切割双链DNA,酶切片段无偏好性
片段化、末端修复/加A一步完成
强扩增效率的高保真酶,显著提高文库质量及产量
适用于FFPE DNA样本
严格的批次性能与稳定性质控
产品组分
组分编号与名称 | 12204ES08 | 12204ES24 | 12204ES96 | ||
12204-A |
| Smearase® Mix | 80 μL | 240 μL | 960 μL |
12204-B | | Ligation Enhancer | 240 μL | 720 μL | 4×720 μL |
12204-C |
| Fast T4 DNA Ligase | 40 μL | 120 μL | 480 μL |
12204-D |
| 2×Ultima Amplification Mix | 200 μL | 600 μL | 4×600 μL |
12204-E |
| Primer Mix | 40 μL | 120 μL | 480 μL |
运输与保存方法
冰袋运输。所有组分-20°C保存,有效期1年。
注意事项
一、关于操作
1. 为了您的安全和健康,请穿实验服并戴一次性手套操作。
2. 请于使用前将试剂盒各组分置于室温解冻。解冻后上下颠倒数次充分混匀,短暂离心后置于冰上待用。
3. 配制各步骤反应液时推荐使用移液器吹打混匀或轻轻振荡,剧烈振荡可能会造成文库产出下降。
4. 为避免样品交叉污染,推荐使用带滤芯的枪头,吸取不同样品时请更换枪头。
5. 推荐在带热盖的PCR仪中进行各步骤反应,使用前应预热PCR仪至反应温度附近。
6. PCR产物因操作不当极容易产生气溶胶污染,进而影响实验结果准确性。推荐将PCR反应体系配制区和PCR产物纯化检测区进行强制性的物理隔离;使用专用的移液器等设备;并定时对各实验区域进行清洁(使用0.5%次氯酸钠或10%漂白剂进行擦拭清理),以保证实验环境的洁净度。
7. 本产品仅作科研用途!
二、关于DNA段化
1. 本试剂盒兼容范围为500 pg – 1 μg Input DNA。应尽可能使用A260/A280 = 1.8-2.0的高质量Input DNA。
2. 若Input DNA中引入高浓度金属离子螯合剂或其他盐,可能会影响后续实验,建议将DNA稀释在ddH2O或不含EDTA的10 mM Tris Buffer (pH 7.5-8.0)中进行片段化。
3. 对于常规的高质量基因组DNA,酶切时间参考表5,本试剂盒片段化偏好低,耐受各种GC含量的模板。对于不同降解程度的FFPE样本,酶切时间参考表6。以上为推荐时间,需客户在自己的实验体系中进行微调,以达到最佳效果。
4.为保证优质精确的片段化效果,片段化反应配制过程请于冰上操作。
5. 针对FFPE DNA建库,若样本质量不佳,客户对当前建库产量不满意,可选购我公司的FFPE DNA Repair Reagent (Cat#12606)对FFPE DNA进行修复,具体使用方法可参考此产品说明书。该试剂可与片段化末修加A过程同时进行,无需额外的操作。
三、关于接头连接 (Adapter Ligation)
1. 针对Illumina®测序平台,Yeasen提供48种Barcoded Adapters: Hieff NGS® Complete Adapter Kit for Illumina®, Set 1~Set 4 (Cat#12615~Cat#12618);单端96种 Index Primers: Hieff NGS® 96 Single Index Primers Kit for Illumina®, Set 1~Set 2 (Cat#12611~Cat#12612);双端384种CDI Primers:Hieff NGS® 384 CDI Primer for Illumina®,Set 1~Set 2 (Cat#12412~Cat#12413);双端384种UDI Primers: Hieff NGS® Stubby UDI Primer Kit for Illumina® (Cat#12404~Cat#12407)。
2. Adapter的质量和使用浓度直接影响连接效率及文库产量。Adapter用量过高可能会产生较多Adapter Dimer;用量较低可能会影响连接效率及文库产量。表1列举了使用本试剂盒,不同Input DNA量推荐的Adapter使用量。
表1 500 pg-1 μg Input DNA推荐的Adapter使用浓度
Input DNA | Adapter : Input DNA摩尔比 | Input DNA | Adapter : Input DNA摩尔比 |
1 μg | 10:1 | 50 ng | 100:1 |
500 ng | 20:1 | 25 ng | 200:1 |
250 ng | 40:1 | 1 ng | 200:1 |
100 ng | 100:1 | 500 pg | 400:1 |
【注】:Input DNA摩尔数 (pmol)≈ Input DNA质量(ng)/ [0.66 × Input DNA平均长度 (bp)]。
四、关于磁珠纯化与分选 (Bead-based Clean Up and Size Selection)
1. DNA段长度分选步骤可选择在末端修复/dA尾添加之前,或接头连接后,或文库扩增后进行。
2. 当Input DNA质量≥50 ng,您可选择在接头连接后分选;如Input DNA质量<50 ng,建议您在文库扩增后进行分选。
3. Ligation Enhancer中包含高浓度的PEG,会对双轮分选产生显著影响。因此,如在接头连接后进行长度分选,必须先进行纯化步骤,再进行双轮分选步骤;如在末端修复/dA尾添加之前或文库扩增后进行长度分选,可直接进行双轮磁珠分选步骤。
4. 磁珠使用前应先平衡至室温,否则会导致得率下降、分选效果不佳。
5. 磁珠每次使用前都应充分振荡混匀或使用移液器上下吹打充分混匀。
6. 转移上清时,请勿吸取磁珠,即使微量残留都将影响后续文库质量。
7. 磁珠漂洗使用的80%乙醇应现用现配,否则将影响回收效率。
8. 进行长度分选时,初始样品体积应尽量≥100 μL,不足时请用超纯水补齐。以防因样品体积太小导致移液误差增大。
9. 产物洗脱前应将磁珠置于室温干燥。干燥不充分容易造成无水乙醇残留影响后续反应;过分干燥又会导致磁珠开裂进而降低纯化得率。通常情况下,室温干燥3-5 min足以让磁珠充分干燥。
10. DNA纯化或长度分选产物如需保存,可使用TE Buffer洗脱,产物可于4°C可保存1-2周,-20°C可保存1个月。
五、关于文库扩增 (Library Amplification)
文库扩增步骤需要严格控制扩增循环数。循环数不足,将导致文库产量低;循环数过多,又将导致文库偏好性增加、重复度增加、嵌合产物增加、扩增突变积累等多种不良后果。表2列举了使用本试剂盒,获得1 μg文库的推荐循环数。
表2 500 pg-1 μg Input DNA获得1000 ng产物扩增循环数推荐表
Input DNA (ng) | Number of cycles required to generate(1000 ng) |
1000 | 2-4 |
500 | 3-5 |
250 | 4-6 |
100 | 5-7 |
50 | 7-8 |
10 | 9-11 |
5 | 10-12 |
1 | 12-14 |
0.5 | 13-15 |
注:上表为使用高质量的Human gDNA构建文库使用的循环数参数。当DNA质量较差或需要进行长度分选,则参照较高循环数进行文库扩增。
六、关于文库质检 (Library Quality Analysis)
1. 通常情况下,构建好的文库可通过长度分布检测和浓度检测来进行质量评价。
2. 文库浓度检测可使用:基于双链DNA荧光染料的方法,如Qubit®、PicoGreen®等;基于qPCR绝对定量的方法。
3. 文库浓度检测不可使用:基于光谱检测的方法,如NanoDrop®等。
4. 推荐使用qPCR方法进行文库浓度检测:Qubit®、PicoGreen®等基于双链DNA荧光染料的浓度测定方法时,无法有效区分单端连接Adapter的产物、两端均未连接Adapter的产物以及其他不完整双链结构产物;qPCR绝对定量基于PCR扩增原理,仅定量样品中两端Adapter完整的文库(即可测序的文库),可排除单端或双端都不连接Adapter的不可测序文库干扰。
5. 文库长度分布检测,可通过Agilent Bioanalyzer 2100等基于毛细管电泳或微控流原理的设备进行检测。
使用方法
一、自备材料
1. 纯化磁珠:Cat#12601,Hieff NGS® DNA Selection Beads或Cat#A63880,AMPure XP Beads或其他等效产品。
2. DNA质控:Agilent Technologies 2100 Bioanalyzer或其他等效产品。
3. DNA Adapter:针对Illumina®测序平台,Yeasen提供48种Barcoded Adapters: Hieff NGS® Complete Adapter Kit for Illumina®, Set 1~Set 4 (Cat#12615~Cat#12618);单端96种 Index Primers: Hieff NGS® 96 Single Index Primers Kit for Illumina®, Set 1~Set 2 (Cat#12611~Cat#12612);双端384种CDI Primers:Hieff NGS® 384 CDI Primer for Illumina®,Set 1~Set 2 (Cat#12412~Cat#12413);双端384种UDI Primers: Hieff NGS® Stubby UDI Primer Kit for Illumina® (Cat#12404~Cat#12407),或其他等效产品。
4. 其他材料:无水乙醇、灭菌超纯水、TE Buffer (10 mM Tris-HCl, pH 8.0-8.5; 0.1 mM EDTA)、低吸附EP管、PCR管、磁力架、PCR仪等。
二、操作流程

图1 OnePot II DNA建库试剂盒操作流程
三、操作步骤
3.1 DNA段化/末端修复/dA尾添加 (DNA Fragment/End Repair/dA-Tailing)
该步骤将基因组DNA段化,同时进行末端修复及dA尾添加。
1. 将表3中各试剂解冻后,颠倒混匀,置于冰上备用。
2. 于冰上配制表3反应体系。
表3 DNA段化/末端修复/dA尾添加 PCR反应体系
名称 | 体积 (μL) |
Input DNA | x |
Smearase® Mix | 10 |
ddH2O | Up to 60 μL |
3. 使用移液器轻轻吹打或低速振荡混匀,并短暂离心将反应液离心至管底。
4. 将上述PCR管置于PCR仪,设置表4所示反应程序,进行DNA段化,末端修复及dA尾添加反应。
表4 DNA段化/末端修复/dA尾添加 PCR反应程序
温度 | 时间 |
热盖105°C | On |
4 °C | 1 min* |
30 °C | 3-20 min** |
72 °C | 20 min |
4 °C | Hold |
【注】:*DNA段化过程为有效控制片段化效果,避免过度酶切,反应程序可预先设置4°C,待模块温度降至4°C时,将PCR管放入PCR仪即可。**对于完整的基因组DNA,酶切时间参考表5;对于质量不一的FFPE DNA样本,酶切时间参考表6。
表5 常规基因组DNA段化时间选择表
插入片段主峰大小 | 片段化时间 | 优化范围 |
600 bp | 5 min | 3-8 min |
350 bp | 8 min | 5-12 min |
250 bp | 10 min | 8-15 min |
200 bp | 13 min | 10-20 min |
150 bp | 20 min | 12-25 min |
表6 FFPE DNA段化时间选择表
插入片段主峰大小 | 片段化时间 | DIN* |
250 bp | 9-13 min | > 8.0 |
250 bp | 8-11 min | 6.5-8.0 |
250 bp | 4-8 min | 4.2-6.5 |
250 bp | 3-6 min | 2.5-4.2 |
【注】:*DIN为DNA Integrity Number,是用Agilent 2200来定义FFPE DNA降解程度的一种方法,详见图2。

图2 Agilent 2200定义不同降解程度样本的DIN值
3.2 接头连接 (Adapter Ligation)
该步骤将3.1步骤的产物末端,连接特定的Illumina®接头。
1. 根据Input DNA量按表1稀释Adapter至合适浓度。
2. 将表7中各试剂解冻后颠倒混匀,置于冰上备用。
3. 于3.1步骤PCR管中配制表7所示反应体系。
表7 Adapter Ligation PCR体系
名称 | 体积 (μL) |
dA-tailed DNA(3.1步骤产物) | 60 |
Ligation Enhancer | 30* |
Fast T4 DNA Ligase | 5 |
DNA Adapter | 5** |
【注】:*Ligation Enhancer比较粘稠,请上下颠倒、振荡,充分混匀并瞬时后离心使用。
**本公司接头浓度与常规商业化试剂盒一致,皆为15 μM。请根据注意事项三中的提示,对接头进行稀释,加水补齐,使接头体积为5 μL。
【接头添加计算举例】:当Input DNA为100 ng,Input DNA长度为300 bp时,接头应该添加多少?
第一步:计算Input DNA摩尔数。公式:Input DNA摩尔数 (pmol)≈ Input DNA质量(ng)/ [0.66 × Input DNA平均长度 (bp)];
Input DNA摩尔数 (pmol)=100÷ (0.66×300)=0.5 pmol;
第二步:计算接头添加摩尔数。根据注意事项三表1查询接头添加比例;
根据表1,查得Input DNA 100 ng时接头添加比例100:1,则接头添加摩尔数=100×0.5 pmol=50 pmol;
第三步:计算接头添加体积。接头浓度=15 μmol/L(如使用其他接头,浓度需要依据其他接头浓度参数);
接头添加体积=接头添加摩尔数 (50 pmol)÷接头浓度 (15 μmol/L)=3.34 μL(注:15 μmol/L=15 pmol/μL)
综上,接头可添加3.4 μL,加1.6 μL水补齐至5 μL。(注:接头最大加入体积不超过5 μL)。
4. 使用移液器轻轻吹打或振荡混匀,并短暂离心将反应液收集至管底。
5. 将PCR管置于PCR仪中,设置表8所示反应程序,进行接头连接反应。
表8 Adapter Ligation PCR反应程序
温度 | 时间 |
热盖 | Off |
20°C | 15 min |
4°C | Hold |
3.3 连接产物磁珠纯化 (Post Ligation Clean Up)
该步骤使用磁珠对3.2步骤的产物进行纯化或分选。纯化可除去未连接的Adapter或Adapter Dimer等无效产物。
3.3.1 纯化操作步骤:
1. 准备工作:将Hieff NGS® DNA Selection Beads磁珠由冰箱中取出,室温平衡至少30 min。配制80%乙醇。
2. 涡旋振荡或充分颠倒磁珠以保证充分混匀。
3. 吸取60 μL Hieff NGS® DNA Selection Beads (0.6×,Beads:DNA=0.6:1)至Adapter Ligation产物中,涡旋振荡或使用移液器轻轻吹打至充分混匀,室温孵育5 min。
4. 将PCR管短暂离心并置于磁力架中分离磁珠和液体,待溶液澄清后(约5 min),小心移除上清。
5. 保持PCR管始终置于磁力架中,加入200 μL新鲜配制的80%乙醇漂洗磁珠,室温孵育30 sec后,小心移除上清。
6. 重复步骤5,总计漂洗两次。最后使用10 μL小枪头吸去残余液体。
7. 保持PCR管始终置于磁力架中,开盖空气干燥磁珠至刚刚出现龟裂(不超过5 min)。
8. 将PCR管从磁力架中取出,进行洗脱:
1)如产物无需进行片段分选,直接加入21 μL ddH2O,涡旋振荡或使用移液器轻轻吹打至充分混匀,室温静置5 min。【注:如纯化产物如需保存,可使用TE Buffer洗脱】。将PCR管短暂离心并置于磁力架中静置,待溶液澄清后(约5 min),小心移取20 μL上清至新PCR管中,切勿触碰磁珠。
2)如产物需进行双轮分选,加入102 μL ddH2O,涡旋振荡或使用移液器轻轻吹打至充分混匀,室温静置5 min。【注:如纯化产物如需保存,可使用TE Buffer洗脱】。将PCR管短暂离心并置于磁力架中静置,待溶液澄清后(约5 min),小心移取100 μL上清至新PCR管中,切勿触碰磁珠。
3.3.2 双轮分选操作步骤:
1. 准备工作:将Hieff NGS® DNA Selection Beads磁珠由冰箱中取出,室温平衡约30 min。配制80%乙醇。
2. 请涡旋振荡或充分颠倒磁珠以保证混匀。
3. 根据DNA段长度要求,参考表9向上述100 μL DNA上清中加入第一轮分选磁珠,涡旋或移液器吹打10次混匀。
表9 磁珠文库分选推荐比例
DNA文库插入片段大小 | 150-250 bp | 200-300 bp | 300-400 bp | 400-500 bp | 500-600 bp |
DNA文库大小 | 250-350 bp | 350-450 bp | 450-550 bp | 550-650 bp | 650-750 bp |
第一轮体积比 (Beads:DNA) | 0.80× | 0.70× | 0.60× | 0.55× | 0.50× |
第二轮体积比 (Beads:DNA) | 0.20× | 0.20× | 0.20× | 0.15× | 0.15× |
【注】:表中“×”表示样品DNA体积。如文库插入片段长度为250 bp,样品DNA体积为100 μL,则第一轮分选磁珠使用体积为0.70×100 μL=70 μL;第二轮分选磁珠使用体积为0.20×100 μL=20 μL;表中所推荐比例是针对于Adapter Ligated Insert DNA (Post Ligation),如果用户在接头连接前进行分选,请采用Hieff NGS® DNA Selection Beads (Cat#12601)说明书中推荐的比例。
4. 室温孵育5 min。
5. 将PCR管短暂离心并置于磁力架中,待溶液澄清后(约5 min),小心转移上清到干净的离心管中。
6. 参考表7向上清中加入第二轮分选磁珠。
7. 涡旋混匀或移液器吹打10次混匀,室温静置5 min。
8. 将PCR管短暂离心并置于磁力架中,待溶液澄清后(约5 min),小心移除上清。
9. 保持PCR管始终处于磁力架中,加入200 μL新鲜配制的80%乙醇漂洗磁珠,室温孵育30 sec,小心移除上清。
10. 重复步骤9,总计漂洗两次。最后使用10 μL小枪头吸去残余液体。
11. 保持PCR管始终处于磁力架中,开盖干燥磁珠至刚刚出现龟裂(约5 min)。
12. 将PCR管从磁力架中取出,加入适量21 μL ddH2O,涡旋振荡或使用移液器轻轻吹打充分混匀,室温静置5 min。
13. 将PCR管短暂离心并置于磁力架中分离磁珠和液体。待溶液澄清后(约5 min),小心转移20 μL上清至干净的管中。
3.4 文库扩增 (Library Amplification)
该步骤将对纯化或长度分选后的接头连接产物进行PCR扩增富集。
1. 将表10中试剂解冻后颠倒混匀,置于冰上备用。
2. 于无菌PCR管中配制表10所示反应体系。
表10 PCR扩增反应体系
名称 | 体积 (μL) |
2×Ultima Amplification Mix | 25 |
Primer mix* | 5 |
Adapter Ligated DNA(3.3步骤产物) | 20 |
【注】:*如果使用的是完整接头(Cat#12615~ Cat#12618),使用试剂盒中的Primer Mix进行扩增;如果使用了不完整的接头(Cat#12611~Cat#12612、Cat#12412~Cat#12413、Cat#12404~Cat#12407),请参照上述试剂盒说明书,使用其中配备的Index Primer进行扩增。
3. 使用移液器轻轻吹打或振荡混匀,并短暂离心将反应液收集至管底。
4. 将PCR管置于PCR仪中,设置表11所示反应程序,进行PCR扩增。
表11 PCR扩增反应程序
温度 | 时间 | 循环数 |
98°C | 1 min | 1 |
98°C | 10 sec | 参照注意事项中表2 |
60°C | 30 sec | |
72°C | 30 sec | |
72°C | 5 min | 1 |
4°C | Hold | - |
3.5 扩增产物磁珠纯化或分选 (Post Amplification Clean Up/Size Selection)
同3.3.1步骤中纯化操作步骤。使用Hieff NGS® DNA Selection Beads (0.9×,Beads:DNA=0.9:1)纯化文库扩增产物。
如需分选,操作方法同3.3.2双轮分选步骤。
3.6 文库质量控制
通常情况下,构建好的文库可通过浓度检测和长度分布检测来进行质量评价,具体请参见注意事项六。
3.7 参考实例
使用Hieff NGS® OnePot II DNA Library Prep Kit for Illumina®对小牛胸腺gDNA样本进行酶切建库检测,片段化结果见图3,建库结果见图3。

图3 OnePot II DNA建库试剂盒酶切800 ng小牛胸腺gDNA样本(不同酶切时间片段化效果检测)

图4 使用本试剂盒进行human gDNA样本建库,文库进行电泳检测
(Input DNA为500 ng,酶切20 min,扩增5 cycles)
HB211215




















